Doté de près de 100 milliards de neurones interconnectés, le cerveau humain est un organe d’une grande complexité dont la modélisation nécessite de couvrir toutes les échelles de la cellule à l’organe. Les pathologies cérébrales sont parfois associées à des atteintes cellulaires qui n’induisent pas nécessairement de modifications visibles dans les IRM acquises à l’hôpital. Il est donc important de se doter de moyens d’imagerie in vivo de cette or- ganisation cellulaire (appelée aussi microstructure). Bien que l’utilisation de très hauts champs ma- gnétiques (>7 teslas) en IRM permette d’accroître la résolution spatiale, elle reste un ordre de grandeur plus faible que la taille des cellules neurales.
Dans le cadre de l’institut franco-allemand AIDAS (https://aidas-lab.eu), l’équipe Ginkgo de NeuroSpin a développé un environnement de simulation numérique complet capable de synthétiser de véritables jumeaux numériques de la microarchitecture du tissu cérébral à partir d’un jeu réduits de paramètres clés de la géométrie des populations de cellules, de simuler le mouvement brownien de l’eau au sein de ces échantillons virtuels, et pour finir simuler la réponse en IRM de diffusion atten- due pour ces échantillons.
PREMIER RÉSULTAT PROMETTEUR
Une campagne de simulation à large échelle menée sur le supercalculateur Joliot-Curie a permis de collecter une large collection d’échantillons représentatifs de la substance blanche cérébrale et de leur signature en IRM de diffusion. Ces Big Data ont ensuite été utilisées pour entraîner un réseau de neurones profond qui contribue à transformer l’IRM en un outil de biopsie virtuelle d’une grande utilité pour diagnostiquer et suivre les pathologies de la substance blanche cérébrale.
Après ce premier résultat prometteur, l’équipe doit prochainement lancer une nouvelle campagne de simulation afin d’établir un second modèle dédié au décodage de la cytoarchitecture du cortex cé- rébral in vivo.
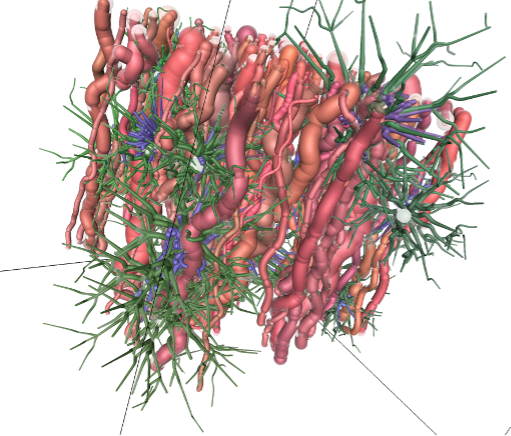
L’illustration montre le résultat de la simulation d’un échantillon de substance blanche cérébrale obtenue avec le simulateur Medusa, comprenant des fibres axonales (en rouge), des astrocytes (en vert) et des oligodendrocytes (en bleu).
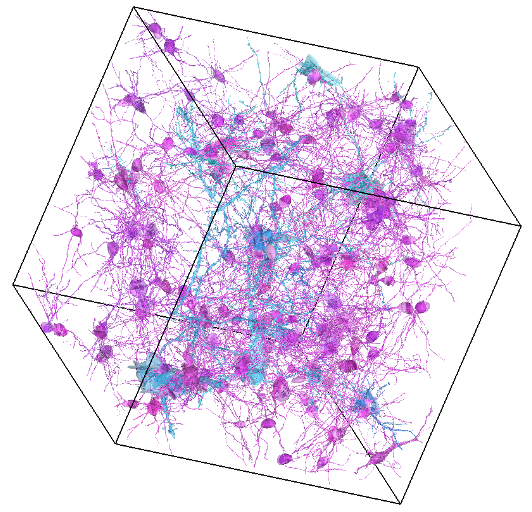
L’illustration montre le résultat de la simulation d’un échantillon de cortex cérébral obtenu avec le simulateur Medusa, comprenant une population de neurones pyramidaux (en bleu) et une population de neurones multipolaires (en violet)